SARS-CoV-2-koronaviruksen genomiseuranta
Päivitetty: 1.7.2025
SARS-CoV-2-virusten evoluutiota on seurattu Suomessa joulukuusta 2020 alkaen niin sanotulla kokogenomisekvensoinnilla. Kokogenomisekvenssien avulla määritetään väestössä kiertävien virusten geneettiset linjat sekä niissä esiintyvät mutaatiot.
THL vastaa Suomessa kansallisesta SARS-CoV-2 genomiseurannasta. Hyvinvointialueiden koronavirusdiagnostiikkaa tukevat laboratoriot toimittavat viikoittain otannan PCR-positiivisista näytteistä sekvensoitavaksi. Tuotettu sekvenssitieto ei sisällä henkilötietoja.
Sekvensoinnin tulokset raportoidaan tartuntatautirekisteriin sekä koosteena tälle sivulle. Sekvenssien perusteella valitaan myös viruksia THL:ssä tapahtuviin laboratoriotutkimuksiin, joissa selvitetään muun muassa viruksen kykyä kiertää immuniteettia.
Suomessa tuotettu sekvenssitieto yhdistetään SARS-CoV-2 virusten maailmanlaajuisiin sekvenssitietokantoihin, joiden avulla pyritään alueellisia muutoksia alalinjojen esiintyvyydessä ja tunnistamaan uusia ja potentiaalisesti pandeemisia alalinjoja.
Sekvensointituloksiin ja Tartuntatautirekisteriin perustuvat tiedot saattavat hieman erota toisistaan johtuen raportointiviiveestä. Viimeisen raportointiviikon tulokset perustuvat usein pieneen näytemäärään ja ovat siten luotettavuudeltaan edeltäviä viikkoja heikompia.
- Havaitut koronavirusmuunnokset jätevedessä
- WHO ja ECDC ylläpitävät listoja tehostetusti seurattavista alalinjoista sekä keräävät tietoa niiden tartuttavuudesta, taudin vakavuudesta sekä kyvystä kiertää immuniteettiä.
Tracking SARS-CoV-2 variants (englanniksi, WHO)
SARS-CoV-2 variants of concern (englanniksi, ECDC) - SARS-CoV-2 alalinjoja maailmalla voi seurata Nextstrain-sivustolla.
Genomic epidemiology of SARS-CoV-2 (englanniksi, Nextrain.org)
Tilannekatsaus, kesäkuu 2025
Genomiseurannassa havaitut SARS-CoV-2 muunnokset ovat omikron BA.2.86 linjasta polveutuvia JN.1 alalinjoja, joista tällä hetkellä yleisimpiä ovat LP.8.1, NB.1.81 ja XEC. Tulokset vastaavat muualla Euroopassa tehtyjä havaintoja.
SARS-CoV-2 viruslinjojen muuntumisen odotetaan jatkuvan uusien, väestön immuniteetin kiertämistä edesauttavien, mutaatioiden myötä. WHO:n tämänhetkisen arvion mukaan, kiertävät koronavirusmuunnokset eivät poikkea vaikuttavuudessaan väestön terveyteen, verrattuna aiempiin muunnoksiin.
Sisältö
- Taulukko 1. SARS-CoV-2 alalinjojen osuudet (%) otosseurannan näytteistä
- Kuvaaja 1. SARS-CoV-2 alalinjajakauma otosseurannassa
- Kuvaaja 2. Pitkän aikavälin kuvaaja tartuntatautirekisteriin kirjattujen linjojen viikoittaisista lukumääristä
Taulukko 1. SARS-CoV-2 alalinjojen osuudet (%) otosseurannan näytteistä
Klikkaa kuva suuremmaksi (png, 173 kt).
Taulukko 1 aineisto saavutettavassa taulukkomuodossa (csv 1 kt)
Kuvaaja 1. SARS-CoV-2 alalinjajakauma otosseurannassa
Klikkaa kuva suuremmaksi (png, 243 kt).Yksilöityjen alalinjojen prosentuaaliset osuudet viikoittaisessa sekvensointiaineistossa, neljän kuukauden seurantajaksolla.
Kuvaajan 1 aineisto saavutettavassa taulukkomuodossa (csv 2 kt)
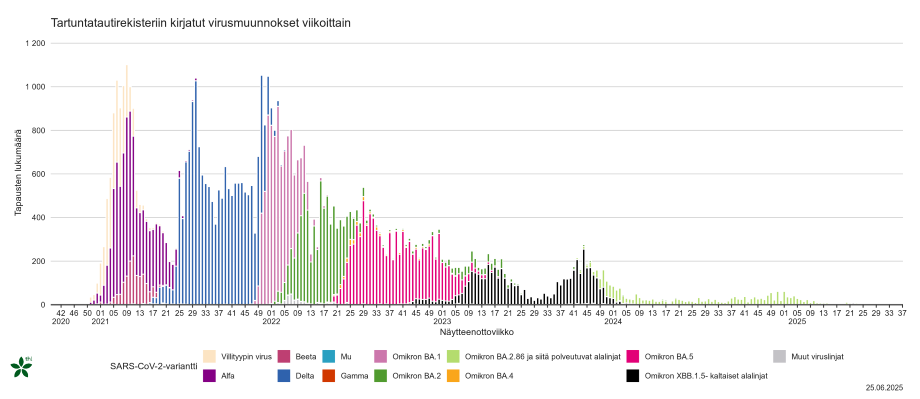
Kuvaaja 2. Pitkän aikavälin kuvaaja tartuntatautirekisteriin kirjattujen linjojen viikoittaisista lukumääristä
Klikkaa kuva suuremmaksi (png, 92 kt). Pitkän aikavälin kuvaaja tartuntatautirekisteriin kirjattujen VOC (Variant of Concern-) viikoittaisista lukumääristä sekvensointiaineistossa. Kuvaajassa esitetään varianttiaaltoja vuoden 2020 lopulta alkaen, jolloin kansallinen SARS-CoV-2 genomiseuranta aloitettiin. Alalinjojen .X-päätteet käsittävät koko alalinjaperheen.
Kuvaajan 2 aineisto saavutettavassa taulukkomuodossa (csv, 121 kt)



.png/47aba589-3d29-5811-89b0-52b9f51ed641?t=1751120208416)